Reaserch article
발효농산물로부터 분리한 사천지역특화 미생물의 다양성 및 특성연구
양주영1,†
,
박미화2,†
,
박지영1
,
간밧손도르1
,
간밧다리마1
,
이용직3
,
이다영4
,
정지원4
,
지원재5
,
조석철6
,
이상재1,*
Diversity and characteristics of specialized microorganisms in the Sacheon region isolated from fermented agricultural products
Joo Young Yang1,†
,
Mi Hwa Park2,†
,
Ji Yeong Park1
,
Sondor Ganbat1
,
Dariimaa Ganbat1
,
Yong-Jik Lee3
,
Da Young Lee4
,
Ji Won Jung4
,
Won-Jae Chi5
,
Seok-Cheol Cho6
,
Sang-Jae Lee1,*
Author Information & Copyright ▼
1신라대학교 바이오식품공학과 & 해양극한미생물연구소
1Department of Food Biotechnology and Research Center for Extremophiles & Marine Microbiology, Silla University, Busan 46958, Korea
2Department of Food and Nutrition, College of Medical and Life Science, Silla University, Busan 46958, Korea
3Department of Bio-Cosmetics, Seowon University, Cheongju 28674, Korea
4Microbial Fermentation Foundation of Sacheon City, Sacheon 52538, Korea
5Biodiversity Research Department, National Institute of Biological Resources, Incheon 22689, Korea
6Department of Food Science & Engineering, Seowon University, Cheongju 28674, Korea
*Corresponding author: Sang-Jae Lee, Department of Food Biotechnology and Research Center for Extremophiles & Marine Microbiology, Silla University, Busan 46958, Korea, E-mail:
sans76@silla.ac.kr
† These authors contributed equally to this work.
ⓒ Copyright 2025 Korean Society for Food Engineering. This is an Open-Access article distributed under the terms of the
Creative Commons Attribution Non-Commercial License (http://creativecommons.org/licenses/by-nc/4.0/) which permits
unrestricted non-commercial use, distribution, and reproduction in any
medium, provided the original work is properly cited.
Received: Nov 09, 2025; Revised: Feb 21, 2025; Accepted: Feb 25, 2025
Published Online: Feb 28, 2025
Abatract
To investigate the diversity of industrially useful microorganisms from fermented agricultural products in the Sacheon region, 128 strains were isolated and analyzed phylogenetically. The analysis indicated that the isolates were categorized into three phyla, eight families, 13 genera, and 33 species. The Bacillaceae family, which was the main taxon, comprised 88.3% of the isolates and included four genera and 22 species: Bacillus, Exiguobacterium, Fictibacillus, and Metabacillus. The Caryophanaceae family, which was the second most abundant taxon, comprised 3.9% of the isolates, including two genera and two species: Rummeliibacillus and Sporosarcina. The isolates were examined for hydrolytic enzyme activity (protease, amylase, and lipase), and 118 strains (92.2%) exhibited at least one of these enzyme activities. Furthermore, auxin production was observed in all seven strains. This study demonstrates that the isolated strains have potential applications in the food and agricultural industries in South Korea, highlighting the importance of genetic resources.
Keywords: Sacheon; Region specialized microorganisms; Diversity; Characteristics; Fermented agricultural products
서 론
사천시는 경상남도 남해에 위치한 다양한 환경적인 특징을 갖는 지역으로 국내에서 산과 들, 해안과 섬, 강과 하천 및 습지가 가장 어우려져 있는 곳이며 겨울이 온화하고 여름이 무더운 남해안 특유의 온대 해양성 기후를 보이며, 사계절의 변화와 자연환경이 어우러져 다양한 기후 경험을 제공하는 특성을 가지고 있으며 복잡한 리아스식 해안을 형성하고 있으며, 경상도 내에서도 뻘이 많은 특이한 지역으로 일반적 내륙 지역과는 환경이 다르다고 할 수 있다. 이와 같은 지리적 환경으로 풍부한 해양 생태계뿐 아니라, 사천 해안가의 특화농업, 작지 않은 규모의 축산업 및 임업 분야 생태계가 골고루 어우러져 있으며, 소위 육해공분야의 산업이 모두 발달되어 있는 지역이다. 나고야 의정서의 생물다양성협약 발효로 인한 사천지역 미생물 자원의 산업분야 활용 가능성을 증가시키기 위한 미생물 자원의 탐색에 관한 연구는 미비한 실정이나 최근 사천시미생물발효재단이 2020년에 설립되어 신라대 EF-Bio 연구실과 함께 사천지역의 해수, 뻘, 하천, 토양, 전통 발효물, 수산물, 축산물, 농산물, 임산물 등과 같은 시료로부터 미생물의 다양성 및 특성 분석 연구가 조금씩 이루어 지고 있다(Lee & Kwak, 1999, Oh & You, 2012; Lee, 2023).
호염성 미생물은 높은 염 농도에서 생육이 가능하며, 이들은 염분 함량이 높은 다양한 자연환경에서 유래하는 경우가 많다. 이러한 미생물들은 분리 및 동정을 통한 계통학적 다양성 연구에 활용될 뿐만 아니라, 여러 천연물을 원료로 한 염장 식품의 풍미 증진과 향미 발달, 그리고 단백질 분해를 위한 효소(protease) 생성 미생물의 특성 규명 연구에도 중요한 역할이 수행되고 있다(Giyatmi & Irianto, 2017; Park et al., 2017; Zang et al., 2020). 또한, 호염성 미생물 및 그들이 생산하는 여러 가수분해 효소는 의약품, 화장품, 식품, 바이오 제품, 세제, 발효물, 섬유 펄프, 피혁 공업품 생산 등의 다양한 산업에서 이미 높은 비율로 사용되고 있으며, 지속적인 개발 연구가 진행되고 있다. 이 미생물과 효소들은 수산물 가공 부산물 및 폐기물의 처리 및 재활용 등 다양한 산업 분야에서도 활용되고 있다(Moreno et al., 2013).
최근에 각 지역마다 지역특화미생물은행을 구축하여 여러 개발과 활용을 모색하고 있다. 본 연구에서는 사천시 지역의 발효농산물에서 호기적으로 호염성 미생물을 순수 분리 · 동정하고 산업적 유용 미생물 활용 가능성을 위한 특성 연구와 미생물이 생산하는 가수분해효소 3종(protease, amylase, lipase)의 활성을 조사하였다. 추가적으로 농업 분야에서 식물 생육을 증진시키는 역할을 하는 옥신(auxin) 생산능의 평가를 통해, 화학비료를 대체할 수 있는 친환경 미생물제제로의 활용 가능성을 검증하고자 하였다. 국내 사천시에서 유래한 호염성 미생물 자원의 확보가 가지는 의의를 바탕으로, 이들을 산업적으로 활용 가능한 생물 소재로서의 가치를 높이는 것을 목표로 하였다.
재료 및 방법
실험 재료
본 연구에 사용된 발효농산물은 사천 지역의 여러 가구의 전통 발효식품을 시료로 확보(Table 1)하였으며 시료의 오염 방지를 위해 위생 장갑을 착용한 후 멸균된 spatula를 사용하여 시료를 채취하였고, 이를 멸균된 50 mL 원추형 튜브에 담아 아이스박스에 보관하여 이동하였다. 실험실에 도착한 후, 실험이 진행되기 전까지 샘플은 4℃에서 보관하였다.
Table 1.
Sacheon regional fermented agricultural products sample list
| No. |
Sample name |
Provider |
Date |
Sampling location |
Category |
Maturation period |
pH |
| 1 |
Soy sauce3 |
In-Seok Cheon |
21.1.17 |
Sacheon-eup |
Household |
18 years |
8 |
| 2 |
Soy sauce1 |
Kongji Eun Farm |
21.1.18 |
Sacheon-si, Sanam-myeon |
Farm |
5 years |
1 |
| 3 |
Soy sauce2 |
Jeong Wol Saem |
21.1.19 |
Jeongdong-myeon, Sogok-gil |
Farm |
13 years |
5 |
| 4 |
Persimmon vinegar |
Choi Jeong-kyung |
21.1.14 |
Sacheon-si, Jeongdong-myeon |
Household |
10 years |
3 |
| 5 |
Wild peach syrup |
Lee Da-Young |
21.1.17 |
Sacheon-eup |
Household |
7 years |
3 |
| 6 |
Ganppang meju |
NH Yonghyeon Agricultural Cooperative |
21.1.14 |
Sacheon-si, Yonghyeon-myeon |
Agricultural cooperative |
2 years |
6 |
| 7 |
Ganppang meju soy sauce |
NH Yonghyeon Agricultural Cooperative |
21.1.14 |
Sacheon-si, Yonghyeon-myeon |
Agricultural cooperative |
4 years |
5 |
| 8 |
Ganppang meju doenjang |
NH Yonghyeon Agricultural Cooperative |
21.1.14 |
Sacheon-si, Yonghyeon-myeon |
Agricultural cooperative |
4 years |
5 |
| 9 |
Gochujang1 |
In-Seok Cheon |
21.1.17 |
Sacheon-eup |
Household |
17 years |
3 |
| 10 |
Gochujang2 |
Kongji Eun Farm |
21.1.18 |
Sacheon-si, Sanam-myeon |
Farm |
7 years |
3 |
| 11 |
Pickled perilla leaves |
Jang Sang-Gwon |
21.1.14 |
Sacheon-eup |
Household |
2 years |
4 |
| 12 |
Dwarfed anchovy sauce |
In-Seok Cheon |
21.1.17 |
Sacheon-eup |
Household |
3 years |
7 |
| 13 |
Dong-a gochujang |
Jang Sang-Gwon |
21.1.14 |
Sacheon-eup |
Household |
2 years |
3 |
| 14 |
Dong-a soy sauce |
Jang Sang-Gwon |
21.1.14 |
Sacheon-eup |
Household |
1 year |
5 |
| 15 |
dong-a doenjang |
Jang Sang-Gwon |
21.1.14 |
Sacheon-eup |
Household |
1 year |
4 |
| 16 |
Doenjang 18 years |
In-Seok Cheon |
21.1.17 |
Sacheon-eup |
Household |
18 years |
5 |
| 17 |
Doenjang 5 years |
Kongji Eun Farm |
21.1.18 |
Sacheon-si, Sanam-myeon |
Farm |
5 years |
4 |
| 18 |
Doenjang 4 years |
Jeong Wol Saem |
21.1.19 |
Jeongdong-myeon, Sogok-gil |
Farm |
4 years |
5 |
| 19 |
Plum fermented tea |
Jang Sang-Gwon |
21.1.14 |
Sacheon-eup |
Household |
1 month |
3 |
| 20 |
Meju |
Kongji Eun Farm |
21.1.18 |
Sacheon-si, Sanam-myeon |
Farm |
1 week |
5 |
| 21 |
Radish kimchi |
In-Seok Cheon |
21.1.18 |
Sacheon-eup |
Household |
1 month |
3 |
| 22 |
Fermented bean curd powder |
NH Yonghyeon Agricultural Cooperative |
21.1.14 |
Sacheon-si, Yonghyeon-myeon |
Agricultural cooperative |
1 year |
5 |
| 23 |
Napa cabbage kimchi |
In-Seok Cheon |
21.1.18 |
Sacheon-eup |
Household |
3 years |
3 |
| 24 |
Wild kiwi sap soy sauce |
Jeong Wol Saem |
21.1.19 |
Jeongdong-myeon, Sogok-gil |
Farm |
12 years |
1 |
| 25 |
Wild kiwi sap doenjang |
Jeong Wol Saem |
21.1.19 |
Jeongdong-myeon, Sogok-gil |
Farm |
6 years |
5 |
| 26 |
Sibjeon daebo tea |
Jang Sang-Gwon |
21.1.14 |
Sacheon-eup |
Household |
1 month |
3 |
| 27 |
Acacia syrup |
In-Seok Cheon |
21.1.17 |
Sacheon-eup |
Household |
6 months |
5 |
| 28 |
Thistle and red plum syrup |
Lee Da-Young |
21.1.17 |
Sacheon-eup |
Household |
5 years |
4 |
| 29 |
Ogapi young shoots pickles |
Wucheon APFarm |
21.1.14 |
Sacheon-si, Sanam-myeon |
Farm |
5 years |
3 |
| 30 |
Mulberry syrup |
In-Seok Cheon |
21.1.17 |
Sacheon-eup |
Household |
7 years |
1 |
| 31 |
Soybean leaf pickles |
Jung Ji Won |
21.1.18 |
Sacheon-eup |
Household |
2 years |
4 |
| 32 |
Green garlic stalk pickles |
Lee Il-geon |
21.1.14 |
Sacheon-si, Miryong Village |
Household |
1 week |
- |
Download Excel Table
사천지역특화 미생물 분리 및 배양
사천시 농협, 농장, 여러 가정집 등에서 모은 32개 발효된 농산물로부터 사천지역특화 호염성 미생물 분리를 위해 각각의 샘플 1 g을 멸균된 0.85% 식염수에 첨가하여 교반기로 교반하여 현탁하였다. 1 mL의 현탁 샘플을 사용해 10배 단위로 10–1에서 10–4까지 단계적으로 희석하였다. 이후 해양 미생물 전용배지인 marine agar (BD, USA)로 일반 배양배지를 준비하여 희석액을 도말하고, 37℃에서 호기성 호염 미생물을 배양하였다. 배양 후, 배지 상에 나타나는 균의 크기, 모양, 색상 등의 형태학적 특성을 관찰한 다음, 동일한 고체배지를 사용해 single colony isolation을 추가적으로 수행하였다. 순수하게 분리된 균주의 혼합배지 내 생육 가능성을 확인하기 위해 nutrient agar (BD, USA), R2A agar (BD, USA), 및 tryptic soy agar (BD, USA) 배지에 평판 도말법으로 37℃에서 7일간 고정 배양을 진행하였다. 또한, 분리된 미생물의 염 농도 및 pH 변화에 따른 생육 가능성을 확인하기 위해 marine agar (BD, USA) 고체배지를 제작하여 37℃에서 생육을 확인하였다. 마지막으로 배양 온도에 따른 생육 여부를 조사하기 위해 marine agar (BD, USA)를 이용하여 25, 30, 35, 40, 45℃에서 배양을 진행하였다(Jeong et al., 2021).
16S rRNA 유전자 DNA염기서열의 계통학적 분석
사천시 농협, 농장, 여러 가정집 등에서 모은 32개의 발효 농산물로부터 호기적 배양 조건으로 분리된 균주들의 분자 생물학적 동정을 위해 각각의 colony를 marine agar (BD, USA) 고체 배지에 배양하여 ㈜마크로젠에 16S rRNA 염기서열 분석을 의뢰하였다. 16S rRNA 유전자는 프라이머 27F (AGAGTTTGATCCTGGCTCAG)와 1492R (CGGTTACCTTGTTACGACTT)을 사용하여 증폭되었다. 결과는 EzBioCloud의 웹사이트(http://www.ezbiocloud.net)에서 제공하는 public nucleotide databases에 있는 16S rRNA 유전자 DNA 염기서열과 비교 및 분석되었다. 계통발생학적 분석(phylogenetic analysis)은 MEGA (version 6) 소프트웨어 패키지에 내장된 Neighbour-joining (NJ) 방법을 이용하여 수행되었다(Lee et al., 2020a).
세포외 분해 효소 생산능 분석
분리된 호염성 미생물의 세포외 분해 효소인 protease, amylase 및 lipase의 생산 능력을 확인하기 위해 각 효소와 특이적으로 반응하는 기질 성분을 포함한 고체 평판 선별 배지를 사용하였다. Protease 생산능 검증을 위해 20% skim milk (BD, USA)를, amylase는 0.2% soluble starch (BD, USA), lipase는 1% Tween 80 (BD, USA)를 기질로 선택하여 marine agar (BD, USA) 배지에 각각 첨가하여 배지를 제조하였다. 이후 분리된 균주를 배지에 접종하고 37℃에서 7일 동안 배양한 후 저지원(clear zone) 직경을 측정하여 분해 효소 활성을 평가하였다. 효소 활성 분해능은 배양 후 나타난 저지원의 크기에 따라 (+++: >7 mm, ++: >4∼6 mm, +: 1∼3 mm) (Table 4)로 기록하였다(Lee et al., 2020a).
옥신(auxin) 생산능 분석
분리된 균주의 auxin 생성 능력을 확인하기 위해 0.1% L-tryptophan (Sigma-Aldrich, USA)이 첨가된 marine broth (BD, USA) 배지에 분리된 순수 colony를 접종하고 37℃에서 5일간 배양하였다. 배양 후 Salkowski 시약(35% HClO4 50 mL+0.5 M FeCl3 1 mL) 800 μL를 배양 상등액 400 μL에 혼합하여 어두운 곳에서 30분 동안 반응시킨 뒤, 535 nm에서 흡광도를 측정하여 옥신 생성 활성을 평가하였다(+++: >1.0, ++: 0.5∼1.0, +: 0.3∼0.5) (Table 4) (Lee et al., 2020a).
결과 및 고찰
호염성 세균 분리
사천시 농협, 농장, 여러 가정집 등에서 모은 32개 발효된 농산물로부터 식품 산업에 활용이 용이할 것으로 생각되는 호기적으로 생육 가능한 사천지역특화 호염성 미생물을 분리하고자 marine agar 배지에 시료를 희석, 도말하여 배양한 후, 배양된 colony의 모양, 색깔, 등 형태학적 특징을 육안으로 구분이 가능한 균주들을 대상으로 동일한 고체배지를 사용하여 2차로 단일 균주 분리를 수행하였다. 그 결과 Table 2에서 나타낸 것처럼 사천지역 장류 시료로부터 86균주와 비장류(장아찌, 과실청 등) 시료로부터 42균주를 분리하여 호염성 미생물 총 128균주를 순수 분리하였다. 또한 주요 성분이 무기염으로 이루어진 marine agar 배지는 해양환경의 호염성 미생물 배양에 유리한 배지이기에 산업적 활용가능성을 확인하기 위하여 대량 배양 등에 많이 활용되는 혼합배지(NA, Nutrient Agar; R2A, Reasoner’s 2A agar; TSA, Tryptic Soy Agar)에서 분리된 균주의 생장능력을 확인한 결과 128균주 중 모든 균주(weak growth 포함)가 적어도 1종류 이상의 산업용 혼합 배지에서 생장이 가능한 것을 확인하였다. 이는 사천지역 발효농산물 시료로부터 천연식물 발효용 halophiles 탐색에 있어서 분리 배지 성분 영향이 어느 정도 미치는 것으로 생각되며, 본 연구 결과를 바탕으로 사천지역 발효농산물 시료로부터 halophiles 분리 최적 배지는 MA (marine agar) 배지로 나타났다. 또한 분리된 균주의 최적 생육 pH를 조사하기 위해 pH 5, 7, 9로 각 조절한 MA 배지에 균주들의 생육을 확인하였다. 산다래수액간장(pH 1, Table 1)으로부터 분리된 JS-65-9를 제외한 127균주가 pH 7에서 생장이 가능(weak growth 포함)하였으며 JS-65-9를 포함한 117균주는 pH 4에서도 생장이 가능(weak growth 포함)하였다(Table 2). 김치, 막걸리, 청국장과 같은 개별 발효식품에서 미생물을 분리 · 동정하는 연구가 다수 수행되었으나, 특정 지역 내 다양한 발효식품에서 분리된 미생물의 분포와 특성을 비교 · 분석하는 연구는 제한적이었다. 최근 순창, 제주, 사천과 같은 지역에서 지역 특화 미생물을 분리 · 동정하고 이를 산업적으로 활용하려는 노력이 활발히 진행되고 있다. 순창의 경우 전통 고추장, 된장, 간장 등의 발효 과정에서 중요한 역할을 하는 미생물들을 집중적으로 연구(Lee et al., 2014)하고 있으며, 2024 발효미생물산업클러스터고도화사업에서 발효 과정의 심화단계 연구를 집중하여 산업화에 적용하고 있다. 반면, 제주에서는 지역의 독특한 환경적 요인(화산토양, 해양 환경 등)이 미생물 다양성에 미치는 영향을 고려하여 미생물을 탐색 · 채집하고, 이를 체계적으로 정리한 '제주토착미생물도감'을 발간(3권)하는 등의 연구를 수행하였다.
Table 2.
Isolation and growth conditions of aerobically cultured halophilic bacteria isolated from the fermented agricultural products on Sacheon city
| No. |
Source |
Isolate |
Media |
MA1) |
| NA2) |
R2A3) |
TSA4) |
NaCl (%) |
Temp. (℃) |
pH |
| 3 |
10 |
25 |
30 |
35 |
40 |
45 |
5 |
7 |
9 |
| 1 |
Soy sauce1 |
HR-66-1 |
+5) |
+ |
+ |
w6) |
w |
+ |
w |
w |
w |
-c7) |
+ |
w |
w |
| 2 |
Soy sauce2 |
JS-66-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
w |
| 3 |
Soy sauce2 |
HR-46-1 |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
w |
| 4 |
Soy sauce3 |
JS-66-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 5 |
Soy sauce3 |
JS-54-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 6 |
Soy sauce3 |
HR-66-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 7 |
Persimmon vinegar |
JY-34-1 |
+ |
w |
+ |
w |
w |
w |
w |
w |
w |
w |
+ |
w |
w |
| 8 |
Wild peach syrup |
HR-38-2 |
+ |
+ |
+ |
+ |
- |
+ |
w |
+ |
w |
w |
+ |
+ |
- |
| 9 |
Ganppang meju |
GH-120-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 10 |
Ganppang meju soy sauce |
JY-18-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 11 |
Ganppang meju soy sauce |
JY-18-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 12 |
Ganppang meju soy sauce |
JY-18-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 13 |
Ganppang meju soy sauce |
JY-18-4 |
w |
w |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
w |
- |
+ |
+ |
| 14 |
Ganppang meju soy sauce |
JY-18-5 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 15 |
Ganppang meju doenjang |
JS-13-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 16 |
Ganppang meju doenjang |
JS-13-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 17 |
Ganppang meju doenjang |
JS-13-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 18 |
Ganppang meju doenjang |
JS-13-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 19 |
Ganppang meju doenjang |
JS-13-5 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 20 |
Ganppang meju doenjang |
JS-13-6 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 21 |
Ganppang meju doenjang |
JS-13-7 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 22 |
Ganppang meju doenjang |
JS-13-8 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 23 |
Ganppang meju doenjang |
JS-13-9 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 24 |
Ganppang meju doenjang |
JS-13-11 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 25 |
Gochujang1 |
JY-48-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
- |
| 26 |
Gochujang1 |
JY-58-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
- |
| 27 |
Gochujang1 |
JY-58-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
- |
| 28 |
Gochujang2 |
JY-48-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 29 |
Gochujang2 |
JY-48-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 30 |
Gochujang2 |
JY-58-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 31 |
Gochujang2 |
JY-48-6 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 32 |
Gochujang2 |
JY-48-7 |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 33 |
Pickled perilla leaves |
JY-30-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
| 34 |
Pickled perilla leaves |
JY-30-2 |
+ |
+ |
+ |
+ |
- |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 35 |
Pickled perilla leaves |
JY-30-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 36 |
Pickled perilla leaves |
JY-30-5 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 37 |
Dwarfed anchovy sauce |
HR-35-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 38 |
Dwarfed anchovy sauce |
HR-35-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 39 |
Dwarfed anchovy sauce |
HR-35-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 40 |
Dong-a gochujang |
JY-26-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 41 |
Dong-a gochujang |
JY-26-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 42 |
Dong-a gochujang |
JY-26-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 43 |
Dong-a gochujang |
JY-26-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 44 |
Dong-a gochujang |
JY-26-5 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 45 |
Dong-a soy sauce |
HR-2-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 46 |
Dong-a soy sauce |
HR-2-6 |
+ |
+ |
+ |
+ |
- |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
- |
| 47 |
Dong-a soy sauce |
GH-2-5 |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
w |
- |
- |
+ |
+ |
| 48 |
Dong-a soy sauce |
HR-2-9 |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 49 |
Dong-a soy sauce |
HR-2-10 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
- |
| 50 |
Dong-a soy sauce |
HR-2-7 |
+ |
+ |
+ |
+ |
- |
+ |
+ |
+ |
+ |
+ |
w |
+ |
+ |
| 51 |
Dong-a soy sauce |
HR-2-8 |
+ |
+ |
+ |
+ |
- |
+ |
+ |
+ |
+ |
+ |
w |
+ |
+ |
| 52 |
Dong-a soy sauce |
HR-2-12 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 53 |
Dong-a soy sauce |
HR-2-13 |
+ |
+ |
w |
+ |
- |
- |
+ |
+ |
w |
w |
+ |
+ |
- |
| 54 |
dong-a doenjang |
HR-1-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 55 |
dong-a doenjang |
HR-1-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 56 |
Doenjang 18 years |
DRM-41-5 |
+ |
+ |
+ |
+ |
- |
+ |
+ |
+ |
+ |
+ |
- |
+ |
+ |
| 57 |
Doenjang 18 years |
DRM-41-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
w |
+ |
+ |
| 58 |
Doenjang 18 years |
DRM-41-2 |
- |
- |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
| 59 |
Doenjang 18 years |
DRM-41-3 |
- |
- |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
| 60 |
Doenjang 18 years |
DRM-41-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 61 |
Doenjang 4 years |
DRM-68-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 62 |
Doenjang 4 years |
DRM-68-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 63 |
Doenjang 4 years |
DRM-68-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 64 |
Doenjang 4 years |
DRM-68-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 65 |
Doenjang 4 years |
DRM-68-5 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 66 |
Doenjang 4 years |
DRM-68-7 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 67 |
Doenjang 5 years |
HR-56-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
- |
| 68 |
Doenjang 5 years |
HR-56-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 69 |
Plum fermented tea |
GH-126-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 70 |
Plum fermented tea |
GH-126-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 71 |
Plum fermented tea |
GH-126-4 |
+ |
+ |
+ |
+ |
- |
w |
w |
+ |
w |
- |
+ |
+ |
- |
| 72 |
Meju |
JS-59-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
w |
| 73 |
Meju |
JS-59-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
w |
| 74 |
Radish kimchi |
JY-61-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 75 |
Radish kimchi |
JY-61-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 76 |
Radish kimchi |
JY-61-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 77 |
Fermented bean curd powder |
jo 15-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 78 |
Fermented bean curd powder |
jo 15-2-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 79 |
Fermented bean curd powder |
jo 15-3 |
+ |
+ |
+ |
w |
- |
+ |
w |
w |
w |
- |
- |
w |
w |
| 80 |
Fermented coffee(1) |
GH-124A-1 |
w |
- |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
- |
+ |
+ |
| 81 |
Fermented coffee(2) |
GH-124B-99 |
w |
+ |
+ |
+ |
w |
+ |
+ |
+ |
w |
w |
w |
+ |
+ |
| 82 |
Napa cabbage kimchi |
JS-62-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 83 |
Wild kiwi extractsoy sauce |
JY-65-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 84 |
Wild kiwi extractsoy sauce |
JY-65-5 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 85 |
Wild kiwi extractsoy sauce |
JY-65-6 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 86 |
Wild kiwi extractsoy sauce |
JY-65-7 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 87 |
Wild kiwi extractsoy sauce |
JY-65-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 88 |
Wild kiwi extractsoy sauce |
JY-65-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 89 |
Wild kiwi extractsoy sauce |
JS-65-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 90 |
Wild kiwi extractsoy sauce |
JS-65-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 91 |
Wild kiwi extractsoy sauce |
JS-65-7 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 92 |
Wild kiwi extractsoy sauce |
JS-65-8 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 93 |
Wild kiwi extractsoy sauce |
JY-65-10 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 94 |
Wild kiwi extractsoy sauce |
JY-65-11 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 95 |
Wild kiwi extractsoy sauce |
JY-65-12 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 96 |
Wild kiwi extractsoy sauce |
JS-65-9 |
+ |
+ |
+ |
- |
+ |
+ |
+ |
- |
+ |
+ |
+ |
- |
- |
| 97 |
Wild kiwi extractsoy sauce |
JY-65-9 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 98 |
Wild kiwi extractsoy sauce |
DRM-67-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 99 |
Wild kiwi extractsoy sauce |
DRM-67-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 100 |
Wild kiwi extractsoy sauce |
DRM-67-5 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 101 |
Wild kiwi extractsoy sauce |
DRM-67-6 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 102 |
Wild kiwi extractsoy sauce |
DRM-67-7 |
+ |
+ |
+ |
+ |
+ |
+ |
w |
+ |
+ |
w |
+ |
+ |
- |
| 103 |
Wild kiwi extractsoy sauce |
DRM-67-8 |
+ |
+ |
+ |
w |
w |
+ |
w |
w |
w |
w |
+ |
w |
- |
| 104 |
Wild kiwi extractsoy sauce |
DRM-67-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 105 |
Sipjeondaebo fermented tea |
GH-127-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 106 |
Sipjeondaebo fermented tea |
GH-127-15 |
+ |
+ |
+ |
+ |
- |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 107 |
Sipjeondaebo fermented tea |
GH-127-16 |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 108 |
Sipjeondaebo fermented tea |
GH-127-2 |
+ |
+ |
+ |
+ |
- |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 109 |
Sipjeondaebo fermented tea |
GH-127-10 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 110 |
Sipjeondaebo fermented tea |
GH-127-11 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 111 |
Seed soy sauce |
JS-101-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 112 |
Seed soy sauce |
JS-101-4 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 113 |
Seed doenjang |
JS-78-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 114 |
Acacia syrup |
jo 43-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 115 |
Acacia syrup |
jo 43-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
w |
+ |
+ |
w |
| 116 |
Thistle and red plum syrup |
jo 39-1 |
+ |
+ |
+ |
+ |
- |
w |
w |
+ |
+ |
+ |
+ |
+ |
- |
| 117 |
Thistle and red plum syrup |
jo 39-5 |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 118 |
Thistle and red plum syrup |
jo 39-2 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 119 |
Ogapi young shoots pickles |
HR-4-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 120 |
Mulberry syrup |
JS-44-1 |
+ |
+ |
w |
w |
w |
w |
w |
w |
w |
w |
+ |
w |
w |
| 121 |
Soybean leaf pickles |
jo 63-1 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 122 |
Soybean leaf pickles |
jo 63-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 123 |
Green garlic stalk pickles |
JY-22-1 |
w |
w |
+ |
+ |
w |
+ |
+ |
+ |
w |
w |
+ |
+ |
+ |
| 124 |
Green garlic stalk pickles |
JY-22-2 |
w |
+ |
w |
+ |
+ |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
| 125 |
Green garlic stalk pickles |
JY-22-3 |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
+ |
| 126 |
Green garlic stalk pickles |
JY-22-5 |
+ |
+ |
+ |
+ |
- |
+ |
+ |
+ |
+ |
+ |
- |
+ |
+ |
| 127 |
Green garlic stalk pickles |
JY-22-7 |
+ |
+ |
+ |
+ |
- |
+ |
+ |
+ |
+ |
w |
+ |
+ |
+ |
| 128 |
Green garlic stalk pickles |
JY-22-8 |
+ |
+ |
w |
+ |
w |
+ |
+ |
+ |
+ |
w |
- |
+ |
+ |
Download Excel Table
이에 반해 사천시미생물발효재단은 순창과 제주 연구의 장점을 결합하여, 사천 지역 내 다양한 발효식품에서 미생물을 분리 · 동정하는 것뿐만 아니라, 산업적 응용 가능성을 고려한 특성 분석을 강조하였다. 이러한 연구를 통해 사천 지역에서 다양한 배지 이용성과 세포외 효소활성을 포함한 산업적 응용성이 높은 128 균주를 확보할 수 있었다. 이는 지역 기반의 미생물 자원을 산업적으로 활용하는 데 있어 중요한 성과로 볼 수 있다.
16S rRNA 유전자 DNA 염기서열의 계통학적 분석
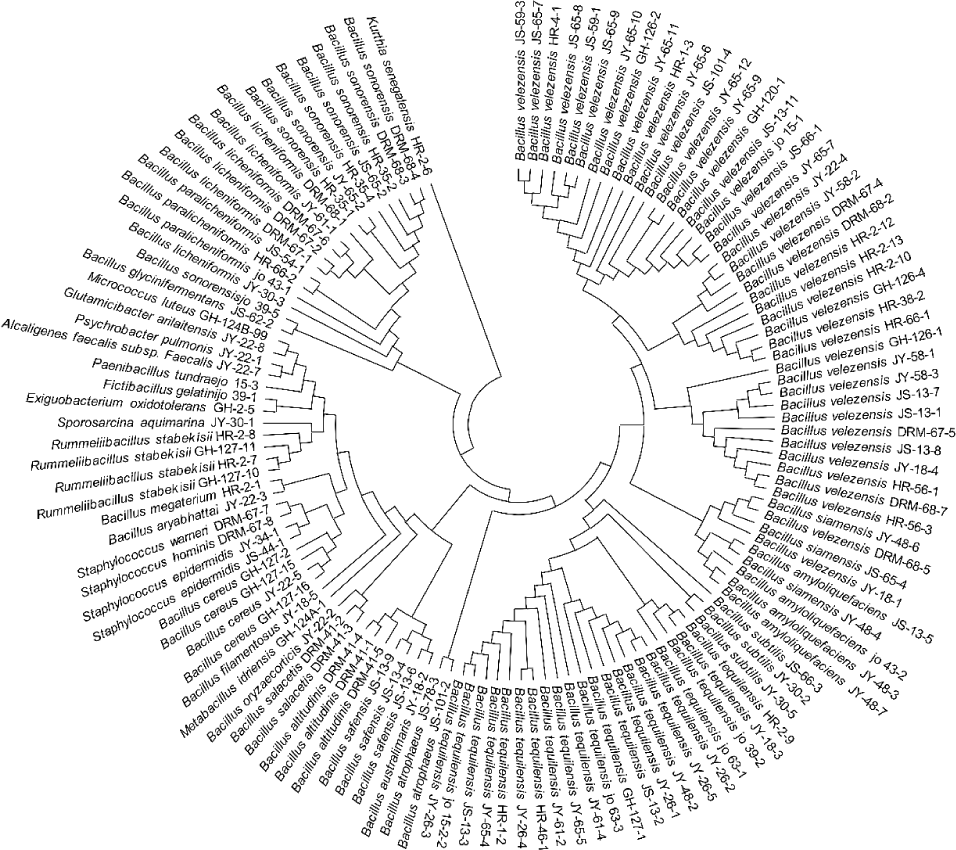
사천시 발효농산물 시료로부터 호기적으로 분리된 128 균주의 16S rRNA 유전자 DNA 염기서열을 기반으로 EzBioCloud를 통해 미생물 동정을 실시하였다. 크게 3문 4강 5목 8과 13속 33종으로 나타났으며(Table 3), 분리 · 동정된 균주, 근연 균주 및 그들의 상동성을 Table 4에 나타내었다. 또한 분리 동정된 균주들 간의 유연관계를 확인하기 위하여 16S rRNA 유전자 DNA 염기서열 계통수를 작성하였다(Fig. 1). Table 3에서 보는 바와 같이 Bacillota (Bacilli)가 96.9%로 우점도가 높았다. 가장 우점도가 높은 Bacillota 문은 Bacillaceae 88.3%, Caryophanaceae 3.9%, Staphylococcaceae 3.1%, Paenibacillaceae 0.8%, Planococcaceae가 0.8%로 구성되었으며, 총 5과 9속 29종이 분리되었다. 본 연구에서 가장 높은 비율로 분리된 Bacillaceae 과 중에서 Bacillus 속은 해양생물과 담수생물에서 많이 분리되며 여러 전통적 발효식품 중에서도 발효농산물과 젓갈류에서 많이 분리된다는 것이 알려져 있다. 이에 복잡한 리아스식 해안을 포함한 다양한 해양환경을 접해 있는 사천시 내의 발효농산물 시료에서 Bacillaceae 과가 가장 많이 분리된 것으로 판단되며(Kim et al., 2013; Ryu et al., 2017; Park et al., 2020), 실제로 사천시 32개 발효농산물 시료 중에 비장류(장아찌, 과실청 등)보다는 장류에서 Bacillaceae과의 호염성 미생물들이 매우 많이 분리되었다. 이는 장류의 발효환경이 고염도인 것이 큰 원인일 것이며, Bacillus와 같은 균주들은 pH 조절과 항균 능력이 우수하여 이와 같은 발효환경에서 많이 발견되는 것이다(Kim et al., 2010; Kim et al., 2013).
Table 3.
Phylum analysis of aerobically cultured halophilic bacteria isolated from the fermented agricultural products in Sacheon city
| Phylum |
Class |
Order |
Family |
Genus |
Species |
No. |
| Actinomycetota |
Actinomycetia |
Micrococcales |
Micrococcaceae |
Glutamicibacter
|
Glutamicibacter arilaitensis
|
1 |
|
|
|
|
|
Micrococcus
|
Micrococcus luteus
|
1 |
| Bacillota |
Bacilli |
Bacillales |
Paenibacillaceae |
Paenibacillus
|
Kurthia senegalensis
|
1 |
|
|
|
|
Planococcaceae |
Kurthia
|
Paenibacillus tundrae
|
1 |
|
|
|
Caryophanales |
Bacillaceae |
Bacillus
|
Bacillus altitudinis
|
3 |
|
|
|
|
|
|
Bacillus amyloliquefaciens
|
4 |
|
|
|
|
|
|
Bacillus aryabhattai
|
1 |
|
|
|
|
|
|
Bacillus atrophaeus
|
2 |
|
|
|
|
|
|
Bacillus australimaris
|
1 |
|
|
|
|
|
|
Bacillus cereus
|
4 |
|
|
|
|
|
|
Bacillus filamentosus
|
1 |
|
|
|
|
|
|
Bacillus glycinifermentans
|
1 |
|
|
|
|
|
|
Bacillus licheniformis
|
6 |
|
|
|
|
|
|
Bacillus megaterium
|
1 |
|
|
|
|
|
|
Bacillus oryzaecorticis
|
1 |
|
|
|
|
|
|
Bacillus paralicheniformis
|
3 |
|
|
|
|
|
|
Bacillus safensis
|
3 |
|
|
|
|
|
|
Bacillus salacetis
|
2 |
|
|
|
|
|
|
Bacillus siamensis
|
3 |
|
|
|
|
|
|
Bacillus sonorensis
|
9 |
|
|
|
|
|
|
Bacillus subtilis
|
3 |
|
|
|
|
|
|
Bacillus tequilensis
|
21 |
|
|
|
|
|
|
Bacillus velezensis
|
41 |
|
|
|
|
|
Exiguobacterium
|
Exiguobacterium oxidotolerans
|
1 |
|
|
|
|
|
Fictibacillus
|
Fictibacillus gelatini
|
1 |
|
|
|
|
|
Metabacillus
|
Metabacillus idriensis
|
1 |
|
|
|
|
Caryophanaceae |
Rummeliibacillus
|
Rummeliibacillus stabekisii
|
4 |
|
|
|
|
|
Sporosarcina
|
Sporosarcina aquimarina
|
1 |
|
|
|
|
Staphylococcaceae |
Staphylococcus
|
Staphylococcus epidermidis
|
2 |
|
|
|
|
|
|
Staphylococcus hominis subsp. hominis |
1 |
|
|
|
|
|
|
Staphylococcus warneri
|
1 |
| Pseudomonadota |
Betaproteobacteria |
Burkholderiales |
Alcaligenaceae |
Alcaligenes
|
Alcaligenes faecalis subsp. Faecalis |
1 |
|
|
Gammaproteobacteria |
Pseudomonadales |
Moraxellaceae |
Psychrobacter
|
Psychrobacter pulmonis
|
1 |
Download Excel Table
Table 4.
Identification and extracellular enzyme productivity of bacteria isolated from the fermented agricultural products in Sacheon city
| No |
Isolate |
Closed strain |
Similarity (%) |
Extracellular enzyme activity |
Auxin |
Deposited number |
| Amylase |
Lipase |
Protease |
| 1 |
HR-66-1 |
Bacillus velezensis
|
100.0 |
- |
- |
- |
- |
NMC9-B49 |
| 2 |
JS-66-1 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B181 |
| 3 |
HR-46-1 |
Bacillus tequilensis
|
99.9 |
- |
++ |
- |
- |
NMC9-B310 |
| 4 |
JS-66-3 |
Bacillus subtilis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B183 |
| 5 |
JS-54-1 |
Bacillus paralicheniformis
|
100.0 |
++ |
- |
++ |
- |
NMC9-B190 |
| 6 |
HR-66-2 |
Bacillus paralicheniformis
|
100.0 |
++ |
- |
+++ |
- |
NMC9-B309 |
| 7 |
JY-34-1 |
Staphylococcus epidermidis
|
99.9 |
- |
- |
+ |
- |
NMC9-B27 |
| 8 |
HR-38-2 |
Bacillus velezensis
|
100.0 |
- |
- |
- |
- |
NMC9-B48 |
| 9 |
GH-120-1 |
Bacillus velezensis
|
100.0 |
+++ |
- |
+++ |
- |
NMC9-B355 |
| 10 |
JY-18-1 |
Bacillus velezensis
|
100.0 |
+++ |
- |
+++ |
- |
NMC9-B135 |
| 11 |
JY-18-2 |
Bacillus australimaris
|
99.9 |
- |
++ |
+++ |
- |
NMC9-B136 |
| 12 |
JY-18-3 |
Bacillus tequilensis
|
99.9 |
- |
+ |
++ |
- |
NMC9-B137 |
| 13 |
JY-18-4 |
Bacillus velezensis
|
99.9 |
- |
- |
+++ |
- |
NMC9-B138 |
| 14 |
JY-18-5 |
Bacillus filamentosus
|
100.0 |
+++ |
- |
+ |
- |
NMC9-B139 |
| 15 |
JS-13-1 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B156 |
| 16 |
JS-13-2 |
Bacillus tequilensis
|
99.7 |
+++ |
++ |
+++ |
- |
NMC9-B157 |
| 17 |
JS-13-3 |
Bacillus tequilensis
|
99.9 |
+++ |
+ |
+ |
- |
NMC9-B158 |
| 18 |
JS-13-4 |
Bacillus safensis
|
99.9 |
- |
- |
+++ |
- |
NMC9-B159 |
| 19 |
JS-13-5 |
Bacillus amyloliquefaciens
|
99.8 |
+++ |
- |
+++ |
- |
NMC9-B160 |
| 20 |
JS-13-6 |
Bacillus safensis
|
99.9 |
- |
+ |
+++ |
- |
NMC9-B161 |
| 21 |
JS-13-7 |
Bacillus velezensis
|
99.8 |
+++ |
- |
+++ |
- |
NMC9-B162 |
| 22 |
JS-13-8 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B163 |
| 23 |
JS-13-9 |
Bacillus safensis
|
99.7 |
- |
+ |
+++ |
- |
NMC9-B164 |
| 24 |
JS-13-11 |
Bacillus velezensis
|
100.0 |
+++ |
- |
+++ |
- |
NMC9-B32 |
| 25 |
JY-48-4 |
Bacillus siamensis
|
99.7 |
+++ |
- |
+++ |
- |
NMC9-B117 |
| 26 |
JY-58-1 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B129 |
| 27 |
JY-58-3 |
Bacillus velezensis
|
99.8 |
+++ |
- |
+++ |
- |
NMC9-B131 |
| 28 |
JY-48-2 |
Bacillus tequilensis
|
99.9 |
++ |
+ |
++ |
- |
NMC9-B109 |
| 29 |
JY-48-3 |
Bacillus amyloliquefaciens
|
99.8 |
+++ |
- |
+++ |
- |
NMC9-B110 |
| 30 |
JY-58-2 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B130 |
| 31 |
JY-48-6 |
Bacillus siamensis
|
100.0 |
+++ |
- |
+++ |
- |
NMC9-B28 |
| 32 |
JY-48-7 |
Bacillus amyloliquefaciens
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B29 |
| 33 |
JY-30-1 |
Sporosarcina aquimarina
|
98.1 |
- |
- |
- |
++ |
NMC9-B121 |
| 34 |
JY-30-2 |
Bacillus subtilis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B122 |
| 35 |
JY-30-3 |
Bacillus licheniformis
|
99.9 |
+ |
- |
++ |
- |
NMC9-B123 |
| 36 |
JY-30-5 |
Bacillus subtilis
|
99.9 |
+ |
- |
+++ |
- |
NMC9-B125 |
| 37 |
HR-35-1 |
Bacillus sonorensis
|
99.3 |
+++ |
- |
+ |
- |
NMC9-B258 |
| 38 |
HR-35-2 |
Bacillus sonorensis
|
99.9 |
+++ |
- |
+ |
- |
NMC9-B259 |
| 39 |
HR-35-4 |
Bacillus sonorensis
|
99.9 |
+++ |
- |
+ |
- |
NMC9-B261 |
| 40 |
JY-26-1 |
Bacillus tequilensis
|
99.9 |
+++ |
+ |
+ |
- |
NMC9-B126 |
| 41 |
JY-26-2 |
Bacillus tequilensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B127 |
| 42 |
JY-26-3 |
Bacillus tequilensis
|
99.9 |
+++ |
- |
+ |
- |
NMC9-B128 |
| 43 |
JY-26-4 |
Bacillus tequilensis
|
99.9 |
+++ |
+ |
+ |
- |
NMC9-B25 |
| 44 |
JY-26-5 |
Bacillus tequilensis
|
99.9 |
+++ |
+ |
+ |
- |
NMC9-B26 |
| 45 |
HR-2-1 |
Bacillus megaterium
|
100.0 |
+++ |
- |
+++ |
+ |
NMC9-B263 |
| 46 |
HR-2-6 |
Kurthia senegalensis
|
60.2 |
+ |
- |
++ |
- |
NMC9-B268 |
| 47 |
GH-2-5 |
Exiguobacterium oxidotolerans
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B424 |
| 48 |
HR-2-9 |
Bacillus tequilensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B43 |
| 49 |
HR-2-10 |
Bacillus velezensis
|
100.0 |
+++ |
- |
+++ |
- |
NMC9-B44 |
| 50 |
HR-2-7 |
Rummeliibacillus stabekisii
|
99.7 |
- |
- |
- |
++ |
NMC9-B452 |
| 51 |
HR-2-8 |
Rummeliibacillus stabekisii
|
100.0 |
- |
- |
+++ |
++ |
NMC9-B453 |
| 52 |
HR-2-12 |
Bacillus velezensis
|
100.0 |
+++ |
- |
+++ |
- |
NMC9-B46 |
| 53 |
HR-2-13 |
Bacillus velezensis
|
100.0 |
+++ |
+ |
+++ |
- |
NMC9-B47 |
| 54 |
HR-1-2 |
Bacillus tequilensis
|
99.9 |
+++ |
++ |
++ |
- |
NMC9-B41 |
| 55 |
HR-1-3 |
Bacillus velezensis
|
99.93 |
+++ |
- |
+++ |
- |
NMC9-B42 |
| 56 |
DRM-41-5 |
Bacillus altitudinis
|
100.0 |
- |
- |
+++ |
- |
NMC9-B436 |
| 57 |
DRM-41-1 |
Bacillus altitudinis
|
99.7 |
- |
+ |
+++ |
- |
NMC9-B95 |
| 58 |
DRM-41-2 |
Bacillus salacetis
|
99.8 |
- |
- |
+++ |
- |
NMC9-B96 |
| 59 |
DRM-41-3 |
Bacillus salacetis
|
99.9 |
- |
- |
+++ |
- |
NMC9-B97 |
| 60 |
DRM-41-4 |
Bacillus altitudinis
|
99.9 |
- |
+ |
+++ |
- |
NMC9-B98 |
| 61 |
DRM-68-1 |
Bacillus licheniformis
|
99.8 |
- |
- |
++ |
- |
NMC9-B104 |
| 62 |
DRM-68-2 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B105 |
| 63 |
DRM-68-3 |
Bacillus sonorensis
|
99.7 |
+++ |
- |
+ |
- |
NMC9-B106 |
| 64 |
DRM-68-4 |
Bacillus sonorensis
|
99.8 |
+++ |
- |
+ |
- |
NMC9-B107 |
| 65 |
DRM-68-5 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B20 |
| 66 |
DRM-68-7 |
Bacillus velezensis
|
99.6 |
+++ |
- |
+++ |
- |
NMC9-B21 |
| 67 |
HR-56-1 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B50 |
| 68 |
HR-56-3 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B51 |
| 69 |
GH-126-1 |
Bacillus velezensis
|
99.8 |
+++ |
- |
+++ |
- |
NMC9-B365 |
| 70 |
GH-126-2 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B366 |
| 71 |
GH-126-4 |
Bacillus velezensis
|
100.0 |
- |
- |
- |
- |
NMC9-B367 |
| 72 |
JS-59-1 |
Bacillus velezensis
|
99.5 |
++ |
- |
+++ |
- |
NMC9-B187 |
| 73 |
JS-59-3 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B189 |
| 74 |
JY-61-1 |
Bacillus licheniformis
|
99.9 |
++ |
- |
+ |
- |
NMC9-B140 |
| 75 |
JY-61-2 |
Bacillus tequilensis
|
99.9 |
+++ |
+ |
+++ |
- |
NMC9-B141 |
| 76 |
JY-61-4 |
Bacillus tequilensis
|
99.9 |
+++ |
+ |
+++ |
- |
NMC9-B143 |
| 77 |
jo 15-1 |
Bacillus velezensis
|
100.0 |
+++ |
- |
+++ |
- |
NMC9-B216 |
| 78 |
jo 15-2-2 |
Bacillus tequilensis
|
99.9 |
++ |
- |
+ |
- |
NMC9-B217 |
| 79 |
jo 15-3 |
Paenibacillus tundrae
|
99.2 |
+++ |
- |
- |
- |
NMC9-B218 |
| 80 |
GH-124A-1 |
Metabacillus idriensis
|
99.5 |
- |
- |
+++ |
- |
NMC9-B361 |
| 81 |
GH-124B-99 |
Micrococcus luteus
|
99.6 |
- |
+ |
+++ |
++ |
NMC9-B362 |
| 82 |
JS-62-2 |
Bacillus glycinifermentans
|
99.9 |
+ |
- |
++ |
- |
NMC9-B191 |
| 83 |
JY-65-4 |
Bacillus tequilensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B112 |
| 84 |
JY-65-5 |
Bacillus tequilensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B113 |
| 85 |
JY-65-6 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B114 |
| 86 |
JY-65-7 |
Bacillus velezensis
|
99.7 |
+++ |
- |
+++ |
- |
NMC9-B115 |
| 87 |
JY-65-3 |
Bacillus sonorensis
|
99.9 |
+++ |
- |
+ |
- |
NMC9-B118 |
| 88 |
JY-65-2 |
Bacillus sonorensis
|
99.9 |
+++ |
- |
++ |
- |
NMC9-B119 |
| 89 |
JS-65-2 |
Bacillus sonorensis
|
99.6 |
+++ |
- |
+ |
- |
NMC9-B174 |
| 90 |
JS-65-4 |
Bacillus siamensis
|
99.7 |
- |
- |
+++ |
- |
NMC9-B176 |
| 91 |
JS-65-7 |
Bacillus velezensis
|
99.8 |
++ |
- |
+++ |
- |
NMC9-B179 |
| 92 |
JS-65-8 |
Bacillus velezensis
|
99.6 |
+++ |
- |
+++ |
- |
NMC9-B180 |
| 93 |
JY-65-10 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B22 |
| 94 |
JY-65-11 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B23 |
| 95 |
JY-65-12 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B24 |
| 96 |
JS-65-9 |
Bacillus velezensis
|
99.6 |
+++ |
- |
+++ |
- |
NMC9-B33 |
| 97 |
JY-65-9 |
Bacillus velezensis
|
99.9 |
++ |
- |
+++ |
- |
NMC9-B64 |
| 98 |
DRM-67-2 |
Bacillus licheniformis
|
99.8 |
- |
- |
++ |
- |
NMC9-B100 |
| 99 |
DRM-67-4 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B101 |
| 100 |
DRM-67-5 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B102 |
| 101 |
DRM-67-6 |
Bacillus licheniformis
|
99.9 |
- |
- |
++ |
- |
NMC9-B103 |
| 102 |
DRM-67-7 |
Staphylococcus warneri
|
99.9 |
- |
+ |
- |
- |
NMC9-B18 |
| 103 |
DRM-67-8 |
Staphylococcus hominis subsp. hominis |
99.8 |
- |
- |
- |
- |
NMC9-B19 |
| 104 |
DRM-67-1 |
Bacillus licheniformis
|
99.6 |
++ |
- |
+++ |
- |
NMC9-B99 |
| 105 |
GH-127-1 |
Bacillus tequilensis
|
100.0 |
+++ |
++ |
+++ |
- |
NMC9-B368 |
| 106 |
GH-127-15 |
Bacillus cereus
|
100.00 |
+++ |
- |
+++ |
- |
NMC9-B369 |
| 107 |
GH-127-16 |
Bacillus cereus
|
100.0 |
+++ |
- |
+++ |
- |
NMC9-B370 |
| 108 |
GH-127-2 |
Bacillus cereus
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B371 |
| 109 |
GH-127-10 |
Rummeliibacillus stabekisii
|
99.9 |
- |
- |
- |
- |
NMC9-B485 |
| 110 |
GH-127-11 |
Rummeliibacillus stabekisii
|
100.0 |
- |
- |
- |
- |
NMC9-B486 |
| 111 |
JS-101-2 |
Bacillus atrophaeus
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B170 |
| 112 |
JS-101-4 |
Bacillus velezensis
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B172 |
| 113 |
JS-78-3 |
Bacillus atrophaeus
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B200 |
| 114 |
jo 43-1 |
Bacillus paralicheniformis
|
99.5 |
+++ |
- |
+++ |
- |
NMC9-B226 |
| 115 |
jo 43-2 |
Bacillus amyloliquefaciens
|
99.9 |
+++ |
- |
+++ |
- |
NMC9-B227 |
| 116 |
jo 39-1 |
Fictibacillus gelatini
|
99.7 |
- |
- |
+++ |
- |
NMC9-B224 |
| 117 |
jo 39-5 |
Bacillus sonorensis
|
99.1 |
++ |
- |
++ |
- |
NMC9-B225 |
| 118 |
jo 39-2 |
Bacillus tequilensis
|
99.6 |
- |
- |
+++ |
- |
NMC9-B37 |
| 119 |
HR-4-1 |
Bacillus velezensis
|
99.6 |
- |
- |
+++ |
- |
NMC9-B269 |
| 120 |
JS-44-1 |
Staphylococcus epidermidis
|
99.9 |
- |
- |
+ |
- |
NMC9-B36 |
| 121 |
jo 63-1 |
Bacillus tequilensis
|
99.9 |
+++ |
++ |
+++ |
- |
NMC9-B38 |
| 122 |
jo 63-3 |
Bacillus tequilensis
|
99.9 |
+++ |
++ |
+++ |
- |
NMC9-B39 |
| 123 |
JY-22-1 |
Psychrobacter pulmonis
|
99.8 |
- |
- |
- |
++ |
NMC9-B144 |
| 124 |
JY-22-2 |
Bacillus oryzaecorticis
|
99.5 |
++ |
- |
+++ |
- |
NMC9-B145 |
| 125 |
JY-22-3 |
Bacillus aryabhattai
|
99.9 |
+++ |
- |
+++ |
+ |
NMC9-B146 |
| 126 |
JY-22-5 |
Bacillus cereus
|
100.0 |
+++ |
- |
+++ |
- |
NMC9-B148 |
| 127 |
JY-22-7 |
Alcaligenes faecalis subsp. Faecalis |
100.0 |
- |
- |
- |
- |
NMC9-B150 |
| 128 |
JY-22-8 |
Glutamicibacter arilaitensis |
99.1 |
- |
- |
++ |
- |
NMC9-B151 |
Download Excel Table
Fig. 1.
Phylogenetic tree analysis based on 16S rRNA gene DNA sequences of bacteria isolated from the fermented agricultural products in Sacheon city. Circular tree based on Neighbor-Joining (NJ) method (Saitou and Nei, 1987) and the evolutionary distances were computed using the Maximum Composite Likelihood method (Tamura et al., 2004). Evolutionary analyses were conducted in MEGA11 (Tamura et al., 2021).
Download Original Figure
Pseudomonadota 문에서는 2과 2속 2종이 분리되었으며 Alcaligenes와 Psychrobacter 속에서 각 1균주씩 분리되었다. 마지막으로, Actinomycetota 문에서는 1과 2속 2종의 Glutamicibacter와 Micrococcus 속에서 각 1균주씩 분리되었다. 분리 균주 중 근연 균주와의 16S rRNA gene DNA 염기서열 상동성이 낮은 균주(96% 이하)는 확인되지 않았다. 본 연구에서 분리된 Bacillus 속 균주 중에서 velezensis와 tequilensis 종은 사천시 내의 장류와 비장류의 다양한 24개 시료로부터 총 62균주(48.4%)가 골고루 동정되었다. 이는 Kim et al. 2010, 2013에서 언급했듯이 사천시 지역의 장기발효식품 내 환경에 잘 적응하고 안정성이 높은 대표적인 균주들이 Bacillus velezensis와 tequilensis라고 생각할 수 있다. 반대로 십전대보차와 풋마늘대 장아찌에서 Bacillus cereus가 발견되었다. 이 균주는 선식과 즉석조리식품에서 꾸준히 발견되어 온 안전하지 않은 균주이다(Kim et al., 2004; Cho et al., 2008). 산업화에 주의를 해야 하는 균주로서, 해당 균주의 생육정도를 정량적으로 더 정확히 살펴봐야 하지만, 산업화에 사용할 때에는 전통적인 지역특화 발효물로부터 표준화된 안전관리(적절한 온도 관리, 철저한 가열 조리, 위생적 취급, HACCP 시스템 도입 등)를 해야 할 필요가 있다.
분해 효소 및 옥신 생산능 분석
해양환경이 풍부하고 인접한 지역의 농산물 발효식품은 고염의 특성, 미네랄 풍부, 풍부한 감칠맛, 해안기후로 인한 발효속도 상승과 발효미생물의 다양성과 함께 다양한 미생물들이 생산하는 효소들에 의해 숙성 과정을 통해 만들어지는 전통 식품으로 알려져 있기에(Voidarou C et al., 2021; Li et al., 2024) 분리된 호염성 미생물 균주들이 식품 산업에서 활용할 수 있는 가수분해 효소 자원으로서의 가능성과 미생물 비료로의 산업적 응용성을 평가하기 위해, 이들의 세포외 가수분해 효소와 옥신 생산 능력을 분석하였다. Table 4에 나타낸 것처럼 분리된 128균주 중 118균주(92.2%)에서 한 가지 이상의 분해 효소 활성이 존재하는 것을 확인하였으며, protease 활성을 보이는 115균주, amylase 활성을 보이는 92균주, lipase 활성을 보이는 22균주를 확보하였고, 이 중 두 가지 이상의 효소 활성을 가지는 98 균주, 세 효소 활성을 모두 갖는 13균주도 확인되었다. 최근 미생물군을 분리하고 세포외 효소활성을 체크한 4편의 논문과 비교하면, 92.2%는 높은 편이다. 대표적인 세포외 효소인 protease, amylase, lipase 중 한 개 이상의 효소활성을 갖는 비율은 국내 염전(신안태평과 곰소) 유래 162균주 중에서 77.2%와 에티오피아 소금(다나킬과 아프데라호수) 유래 68균주 중에서 79.4% (Lee et al., 2020), 제주 해안근처 목장(양떼, 녹원 및 아침미소) 유래 116균주 중에서 77.6% (Lee et al., 2020), 국내외 수산물(남해, 서남해 및 대마도) 유래 86균주 중에서 64.0%(Jeong et al., 2021), 제주 남서해안 토양(화순항과 대포포구) 유래 46균주 67.4% (Lee et al., 2022)이었다.
미생물이 생산하는 옥신(Indole-3-Acetic Acid, IAA)은 식물의 생장과 발달에 중요한 역할을 한다고 알려져 있다. 옥신은 식물의 세포 신장, 분화, 발아, 뿌리 발달, 과실 성장, 광합성 활성 증가, 스트레스 저항성 증가, 질소 고정화 등을 촉진하여 전반적인 생장 증진에 기여한다고 알려져 있다(Woo et al., 2007). 분리된 균주의 옥신 생산능을 확인한 결과, 장류(동아간장) 시료에서 분리한 Bacillus megaterium HR-2-1, Rummeliibacillus stabekisii HR-2-7 & HR-2-8 의 3균주와 비장류(깻잎 장아찌, 발효커피(2), 풋마늘대 장아찌) 시료에서 분리된 Sporosarcina aquimarina JY-30-1, Micrococcus luteus GH-124B-99, Bacillus aryabhattai JY-22-3 & Psychrobacter pulmonis JY-22-1균주 포함 총 7균주에서 옥신 생산능이 확인되었다. 본 연구의 결과는 사천 지역 발효 농산물 시료로부터 국내 미생물 자원의 다양성을 확보하는 데 중요한 의의를 지닐 수 있으며, 또한 산업용 가수분해 효소 관련 생물공학 및 친환경 미생물 제제 개발을 위한 기초 생물소재로 활용될 가능성이 기대된다. 또한 본 연구를 통하여 분리한 모든 균주들은 한국생명공학연구원(KRIBB) 미생물가치제고사업단에 기탁하였다.
요 약
본 연구는 산업적으로 유용한 미생물을 동정하고 특성 분석하기 위해 사천지역 내의 32개 발효농산물로부터 128균주를 순수 분리하였다. 분리된 균주들을 16S rRNA gene DNA 염기서열 분석을 바탕으로 계통학적으로 분석한 결과, 3문, 8과, 13속, 33종으로 구성되어 있는 것을 확인하였다. 특히, Bacillaceae 과는 88.3%를 차지하며, 4개의 속(Bacillus, Exiguobacterium, Fictibacillus 및 Metabacillus 속)과 22개의 종으로 구성되었다. 두 번째 그룹의 Caryophanaceae 과는 3.9%를 차지하며, 2개의 속(Rummeliibacillus and Sporosarcina 속)과 2개의 종으로 구성되었다. 분리된 균주들의 가수 분해 효소 활성을 조사한 결과, 118개 균주(92.2%)가 적어도 하나의 효소 활성을 보였다. 이는 상당히 높은 비율이다. 또한, 7개의 균주에서 옥신 생산 능력이 확인되었다. 본 연구는 분리된 균주들이 사천시의 지역특화미생물로서 식품 및 농업뿐 아니라 여러 산업에서 활용될 가능성과 유전자원의 중요성이 있음을 보여주고 있다.
Acknowledgements
This paper was supported by the Phase 3 Industry-Academia Collaboration Leading University Development Project (LINC 3.0) funded by the Ministry of Education and the National Research Foundation of Korea, as well as by the Sacheon Microbial Fermentation Foundation, supported by the city of Sacheon, and the University Innovation Research Complex Project (20240002) funded by Busan Technopark. It was also supported by the National Institute of Biological Resources (NIBR202402105) under the Ministry of Environment.
Authorship contribution statement
References
Kim TS, Lee GH, Kim GJ, Lee SW, Park K and Park JW. 2010. Antifungal activity of bacterial strains isolated from tidal mudflat and salted seafood (traditional jeotgal) against six major plant pathogens. Korean J. Pestic. Sci. 14: 421-426.

Kim HR, Han S, Lee B, Jeong DW and Lee JH. 2013. Analysis of the bacterial community in ojingeo-jeotgal and selection of
Bacillus species inhibiting the growth of food pathogens. Korean J. Microbiol. Biotechnol. 41: 462-468.


Lee J and Kwak CH. 1999. The historical geography of Sacheon bay region. J. Korean Assoc. Reg. Geogr. 5: 119-132.

Lee YD. 2023. A study on flor and management of village forests in Sacheon-si, Gyeongsangnam-do. MS thesis, Gyeongsang National Univ.

Oh HK and You JH. 2012. The basic study for developing plant ecological indices of Sacheon-si, Gyeongsangnam-do. J. Environ. Impact Assess. 21: 509-523.

Park WJ, Lee SH, Lee HJ. 2017. Antibacterial and proteolytic activities of bacterial isolates from ethnic fermented seafoods in the east coast of Korea. Food Eng. Prog. 21: 88-92.


Park KS, Cho ED, Kim HD. 2020. Profiles of toxin genes and antimicrobial resistance of
Bacillus cereus strains isolated from commercial Jeotgal. J. Fish. Aquat. Sci. 53: 870-877.

Ryu MS, Yang HJ, Kim JW, Jeong SJ, Jeong SY, Eom JS and Jeon DY. 2017. Potential probiotics activity of
Bacillus spp. from traditional soybean pastes and fermentation characteristics of Cheonggukjang. Korean J. Food Preserv. 24: 1168-1179.


Saitou N, Nei M. 1987. The neighbor-joining method: a new method for reconstructing phylogenetic trees. Mol. Biol. Evol. 4: 406-425.

Lee SJ, Kim MJ, Park SJ. 2014. Method for preparing low-salt soy sauce. KR101482068B1 Korea.

Lee YJ, Shin KS, Lee SJ. 2020a. A study of the diversity and profile for enzyme production of aerobically cultured halophilic microorganisms from the various solar salterns. Food Eng. Prog. 24: 62-76.


Lee YJ, Shin KS, Lee SJ. 2020b. A research on the diversity and enzyme productivity of halophilic microorganisms isolated from the soil around the ranch for the exploration of fermentation strains. Food Eng. Prog. 24: 77-87.


Jeong GE, Ganbat D, Yeom YJ, Choi BG, Lee HS, Park MH, Shin KS, Lee YJ, Lee SJ. 2021. A study on the characterization of halophilic microorganisms isolated from fermented seafood. Food Eng. Prog. 25: 110-117.


Lee YJ, Ganbat D, Jeong GE, Shin KS, Lee SJ. 2022. A study on the isolation and characterization of aerobic halophilic microorganisms isolated from the soil around the port on Jeju island. Food Eng. Prog. 26: 140-146.


Woo SM, Kim SD. 2007. Confirmation of non-siderophore antifugal substance and cellulase from
Bacillus licheniformis K11 containing antagonistic ability and plant growth promoting activity. J. Life Sci. 17: 983-989.


Kim SH, Kim MG, Kang MC, Son YW, Lee CH, Kim IB, Lee YJ, Choi SY. 2004. Isolation and growth pattern of
Bacillus cereus from ready-to-eat foods. J. Life Sci. 14: 664-669.


Cho YS, Jung EY, Lee MK, Yang CY, Shin DB. 2008. Survival, isolation and characterization of
Bacillus cereus from Sunshik. J. Food Hyg. Safety 23: 343-347.